| Multiple Linear Regression - Estimated Regression Equation |
| PassengersBRU[t] = + 1046423.8 -55056.5944444449M1[t] -26964.7222222221M2[t] + 197427.95M3[t] + 378269.222222222M4[t] + 458309.094444444M5[t] + 476887.966666667M6[t] + 723003.238888889M7[t] + 612347.311111111M8[t] + 549024.983333333M9[t] + 392131.855555556M10[t] + 117328.327777778M11[t] + 2393.52777777778t + e[t] |
| Multiple Linear Regression - Ordinary Least Squares | |||||
| Variable | Parameter | S.D. | T-STAT H0: parameter = 0 | 2-tail p-value | 1-tail p-value |
| (Intercept) | 1046423.8 | 39446.619714 | 26.5276 | 0 | 0 |
| M1 | -55056.5944444449 | 47989.020536 | -1.1473 | 0.257075 | 0.128537 |
| M2 | -26964.7222222221 | 47917.321202 | -0.5627 | 0.57629 | 0.288145 |
| M3 | 197427.95 | 47852.357805 | 4.1258 | 0.00015 | 7.5e-05 |
| M4 | 378269.222222222 | 47794.157814 | 7.9145 | 0 | 0 |
| M5 | 458309.094444444 | 47742.745961 | 9.5996 | 0 | 0 |
| M6 | 476887.966666667 | 47698.144198 | 9.998 | 0 | 0 |
| M7 | 723003.238888889 | 47660.371644 | 15.1699 | 0 | 0 |
| M8 | 612347.311111111 | 47629.444546 | 12.8565 | 0 | 0 |
| M9 | 549024.983333333 | 47605.376245 | 11.5328 | 0 | 0 |
| M10 | 392131.855555556 | 47588.177149 | 8.2401 | 0 | 0 |
| M11 | 117328.327777778 | 47577.854707 | 2.466 | 0.017367 | 0.008683 |
| t | 2393.52777777778 | 572.231258 | 4.1828 | 0.000125 | 6.2e-05 |
| Multiple Linear Regression - Regression Statistics | |
| Multiple R | 0.968492495041633 |
| R-squared | 0.937977712951967 |
| Adjusted R-squared | 0.922142235407788 |
| F-TEST (value) | 59.2326761434978 |
| F-TEST (DF numerator) | 12 |
| F-TEST (DF denominator) | 47 |
| p-value | 0 |
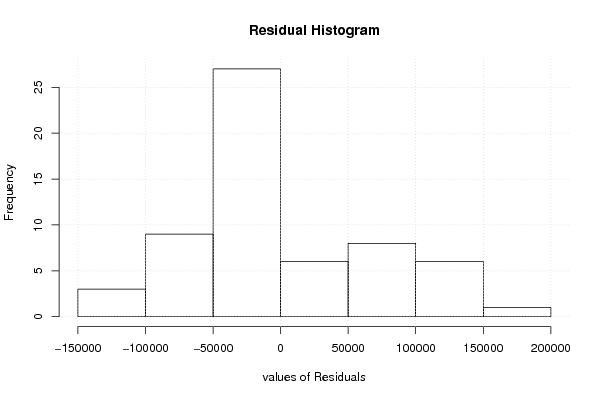
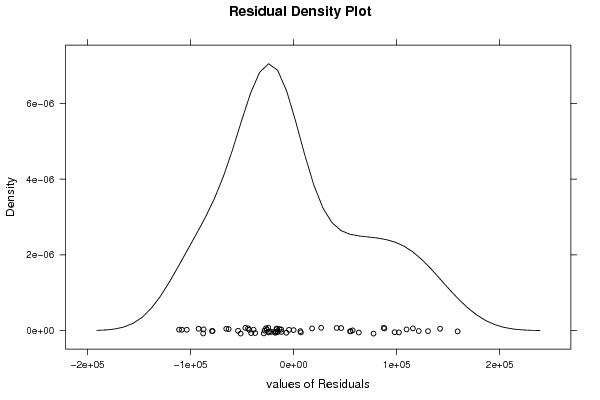
| Multiple Linear Regression - Residual Statistics | |
| Residual Standard Deviation | 75221.7523381548 |
| Sum Squared Residuals | 265940665166.667 |
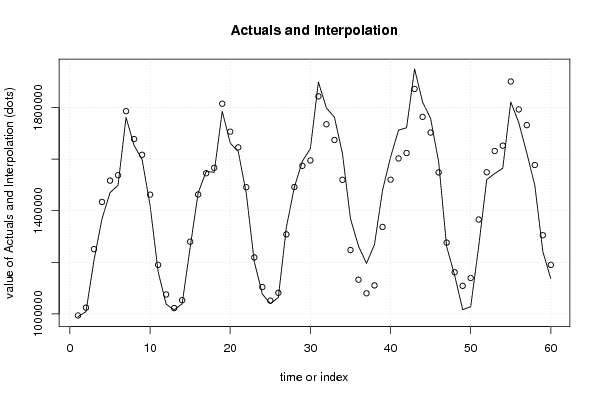
| Multiple Linear Regression - Actuals, Interpolation, and Residuals | |||
| Time or Index | Actuals | Interpolation Forecast | Residuals Prediction Error |
| 1 | 989236 | 993760.733333335 | -4524.7333333352 |
| 2 | 1008380 | 1024246.13333333 | -15866.1333333334 |
| 3 | 1207763 | 1251032.33333333 | -43269.3333333334 |
| 4 | 1368839 | 1434267.13333333 | -65428.1333333333 |
| 5 | 1469798 | 1516700.53333333 | -46902.5333333334 |
| 6 | 1498721 | 1537672.93333333 | -38951.9333333333 |
| 7 | 1761769 | 1786181.73333333 | -24412.7333333333 |
| 8 | 1653214 | 1677919.33333333 | -24705.3333333334 |
| 9 | 1599104 | 1616990.53333333 | -17886.5333333331 |
| 10 | 1421179 | 1462490.93333333 | -41311.9333333332 |
| 11 | 1163995 | 1190080.93333333 | -26085.9333333333 |
| 12 | 1037735 | 1075146.13333333 | -37411.1333333332 |
| 13 | 1015407 | 1022483.06666667 | -7076.06666666607 |
| 14 | 1039210 | 1052968.46666667 | -13758.4666666666 |
| 15 | 1258049 | 1279754.66666667 | -21705.6666666666 |
| 16 | 1469445 | 1462989.46666667 | 6455.53333333338 |
| 17 | 1552346 | 1545422.86666667 | 6923.13333333342 |
| 18 | 1549144 | 1566395.26666667 | -17251.2666666666 |
| 19 | 1785895 | 1814904.06666667 | -29009.0666666666 |
| 20 | 1662335 | 1706641.66666667 | -44306.6666666666 |
| 21 | 1629440 | 1645712.86666667 | -16272.8666666667 |
| 22 | 1467430 | 1491213.26666667 | -23783.2666666666 |
| 23 | 1202209 | 1218803.26666667 | -16594.2666666666 |
| 24 | 1076982 | 1103868.46666667 | -26886.4666666666 |
| 25 | 1039367 | 1051205.4 | -11838.3999999995 |
| 26 | 1063449 | 1081690.8 | -18241.7999999999 |
| 27 | 1335135 | 1308477 | 26658 |
| 28 | 1491602 | 1491711.8 | -109.799999999995 |
| 29 | 1591972 | 1574145.2 | 17826.8 |
| 30 | 1641248 | 1595117.6 | 46130.4 |
| 31 | 1898849 | 1843626.4 | 55222.6 |
| 32 | 1798580 | 1735364 | 63216 |
| 33 | 1762444 | 1674435.2 | 88008.8 |
| 34 | 1622044 | 1519935.6 | 102108.4 |
| 35 | 1368955 | 1247525.6 | 121429.4 |
| 36 | 1262973 | 1132590.8 | 130382.2 |
| 37 | 1195650 | 1079927.73333333 | 115722.266666667 |
| 38 | 1269530 | 1110413.13333333 | 159116.866666667 |
| 39 | 1479279 | 1337199.33333333 | 142079.666666667 |
| 40 | 1607819 | 1520434.13333333 | 87384.8666666667 |
| 41 | 1712466 | 1602867.53333333 | 109598.466666667 |
| 42 | 1721766 | 1623839.93333333 | 97926.0666666667 |
| 43 | 1949843 | 1872348.73333333 | 77494.2666666666 |
| 44 | 1821326 | 1764086.33333333 | 57239.6666666666 |
| 45 | 1757802 | 1703157.53333333 | 54644.4666666666 |
| 46 | 1590367 | 1548657.93333333 | 41709.0666666666 |
| 47 | 1260647 | 1276247.93333333 | -15600.9333333333 |
| 48 | 1149235 | 1161313.13333333 | -12078.1333333334 |
| 49 | 1016367 | 1108650.06666667 | -92283.0666666663 |
| 50 | 1027885 | 1139135.46666667 | -111250.466666667 |
| 51 | 1262159 | 1365921.66666667 | -103762.666666667 |
| 52 | 1520854 | 1549156.46666667 | -28302.4666666668 |
| 53 | 1544144 | 1631589.86666667 | -87445.8666666667 |
| 54 | 1564709 | 1652562.26666667 | -87853.2666666667 |
| 55 | 1821776 | 1901071.06666667 | -79295.0666666667 |
| 56 | 1741365 | 1792808.66666667 | -51443.6666666667 |
| 57 | 1623386 | 1731879.86666667 | -108493.866666667 |
| 58 | 1498658 | 1577380.26666667 | -78722.2666666668 |
| 59 | 1241822 | 1304970.26666667 | -63148.2666666668 |
| 60 | 1136029 | 1190035.46666667 | -54006.4666666668 |
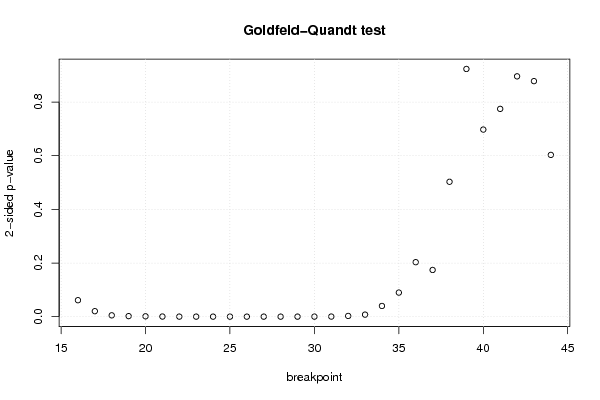
| Goldfeld-Quandt test for Heteroskedasticity | |||
| p-values | Alternative Hypothesis | ||
| breakpoint index | greater | 2-sided | less |
| 16 | 0.0306945672352756 | 0.0613891344705512 | 0.969305432764724 |
| 17 | 0.0102126958972082 | 0.0204253917944165 | 0.989787304102792 |
| 18 | 0.00249280108633591 | 0.00498560217267182 | 0.997507198913664 |
| 19 | 0.00100204598152835 | 0.0020040919630567 | 0.998997954018472 |
| 20 | 0.000655926307042261 | 0.00131185261408452 | 0.999344073692958 |
| 21 | 0.000205023895720114 | 0.000410047791440227 | 0.99979497610428 |
| 22 | 6.40178952850278e-05 | 0.000128035790570056 | 0.999935982104715 |
| 23 | 2.12106220977289e-05 | 4.24212441954578e-05 | 0.999978789377902 |
| 24 | 9.91500346851211e-06 | 1.98300069370242e-05 | 0.999990084996532 |
| 25 | 6.5457480787722e-06 | 1.30914961575444e-05 | 0.999993454251921 |
| 26 | 4.70389379977967e-06 | 9.40778759955933e-06 | 0.9999952961062 |
| 27 | 8.76409790421142e-06 | 1.75281958084228e-05 | 0.999991235902096 |
| 28 | 8.76767665632982e-06 | 1.75353533126596e-05 | 0.999991232323344 |
| 29 | 9.39211096578133e-06 | 1.87842219315627e-05 | 0.999990607889034 |
| 30 | 3.9817474157732e-05 | 7.9634948315464e-05 | 0.999960182525842 |
| 31 | 0.000166518347364995 | 0.000333036694729991 | 0.999833481652635 |
| 32 | 0.00128667368735134 | 0.00257334737470269 | 0.998713326312649 |
| 33 | 0.00379700713029599 | 0.00759401426059198 | 0.996202992869704 |
| 34 | 0.0199202742439781 | 0.0398405484879562 | 0.980079725756022 |
| 35 | 0.0448416559328392 | 0.0896833118656784 | 0.95515834406716 |
| 36 | 0.101550193773449 | 0.203100387546898 | 0.898449806226551 |
| 37 | 0.0870586431540711 | 0.174117286308142 | 0.912941356845929 |
| 38 | 0.251392068590792 | 0.502784137181583 | 0.748607931409208 |
| 39 | 0.461747770129652 | 0.923495540259304 | 0.538252229870348 |
| 40 | 0.348746555510781 | 0.697493111021561 | 0.65125344448922 |
| 41 | 0.387312281542639 | 0.774624563085279 | 0.61268771845736 |
| 42 | 0.447978110211687 | 0.895956220423375 | 0.552021889788313 |
| 43 | 0.439064835949506 | 0.878129671899011 | 0.560935164050494 |
| 44 | 0.301552693473766 | 0.603105386947532 | 0.698447306526234 |
| Meta Analysis of Goldfeld-Quandt test for Heteroskedasticity | |||
| Description | # significant tests | % significant tests | OK/NOK |
| 1% type I error level | 16 | 0.551724137931034 | NOK |
| 5% type I error level | 18 | 0.620689655172414 | NOK |
| 10% type I error level | 20 | 0.689655172413793 | NOK |